| Úprava konců a připojení adaptérů | zobrazit -> |
| Přečištění NGS knihovny a výběr velikosti | zobrazit -> |
| Protokol pro amplifikaci DNA knihovny | zobrazit -> |
| Kvantifikace DNA knihovny | zobrazit -> |
Základní postup při sestavování NGS knihoven
V prvotní fázi jsou upraveny konce fragmentované DNA, přičemž se zatupí 5' - a 3' - přesahy, fosforylují se 5' - konce a jeden dA přesah je přidán na 3' - konec každého fragmentu. Následně se ke každému konci takto upravených DNA fragmentů přidají Illumina™ kompatibilní NGS adaptéry. ClaSeek™ Library Preparation kit můžete navíc použít dohromady s kitem MagJET™ NGS Cleanup a Size Selection, díky čemuž si budete moci vybrat DNA knihovnu pro sekvenování v požadovaném intervalu délky čtení.
Kvalita DNA hraje v přípravě knihovny klíčovou roli
Kvalita a také množství výchozí DNA velmi ovlivní celkovou úspěšnost přípravy DNA knihovny a výsledky sekvenování. Dalšími důležitými faktory, které ovlivní výsledky, je správné zacházení se vzorky, metoda izolace DNA a vyhodnocení koncentrace DNA. Zbytkové stopy kontaminujících proteinů, organických rozpouštědel a jejich solí mohou degradovat DNA nebo snižovat aktivitu enzymů, které jsou nezbytné pro efektivní přípravu DNA knihovny. Jednořetězcová DNA, RNA nebo volné nukleotidy mohou interferovat s přesnou kvantifikací přečištěné DNA, především při použití metody UV spektrometrie.
Důležitá doporučení pro fragmentaci DNA
Protokol pro konstrukci knihovny vyžaduje fragmentovanou DNA získanou jakoukoliv fyzikální metodou, například za pomoci ultrazvuku nebo nebulizace. Kvalitu fragmentované DNA vždy ověřte elektroforézou v agarózovém gelu a také pomocí Agilent 2100 Bioanalyzer®. Protokol fragmentace optimalizujte tak, abyste získali fragmenty střední velikosti.
| Délka čtení NGS knihovny | 50bp nebo 2×25bp | 300bp nebo 2×150bp | 500bp nebo 2×250bp |
| Doporučená střední velikost fragmentované DNA | 200bp | 300-400bp | 500-600bp |
Na co nezapomenout při fragmentaci DNA:
- protokol pro konstrukci DNA knihovny je optimalizován pro vysoce kvalitní fragmentovanou dvouvláknovou DNA, která může být rozpuštěná ve vodě (bez nukleáz), 10mM Tris (pH 7,5-8,5) nebo TE pufru (10mM Tris - Cl, pH 8,0, 1mM EDTA)
- vzorky DNA musí být bez kontaminujících proteinů, RNA, organických rozpouštědel a solí (u vzorků DNA s neznámou kvalitou doporučujeme přečištění)
- pro purifikaci vysoce kvalitní gDNA z různých zdrojů použijte specializované komerční kity, například Thermo Scientific GeneJET Genomic DNA Purification Kit (Cat. #K0721/2), GeneJET Viral DNA a RNA purification Kit (Cat. #K0821), nebo MagJET Genomic DNA Kit (Cat. #K2721/2), MagJET Viral DNA a RNA Kit (Cat. #K2781/2)
- dodržujte pravidla správné laboratorní praxe s cílem minimalizovat křížovou kontaminaci produktů
- roztoky před použitím rozmrazujte na ledě a udržujte je na něm, dokud nejsou připraveny k použití
- provádějte přečištění DNA knihovny, odstranění adaptérů a výběr velikosti ve zkumavkách DNA LoBind™ (Eppendorf ™ Cat. # 022431021)
- roztoky důkladně promíchejte na vortexu před každým použitím
| přístroj pro enzymatickou nebo fyzikální fragmentaci DNA | Illumina ™ kompatibilní adaptéry (s příslušnými indexy, pokud bude v jednom běhu MiSeq™ nebo HiSeq™ sekvenováno více knihoven) |
| 0,5 nebo 0,2 ml PCR zkumavky / destičky | zkumavky LoBind™ 1,5 ml (Cat. # 02243102, Eppendorf™) |
| špičky a pipety | mikrocentrifuga |
| termocykler | vortex |
| real-time termocykler | komerčně dostupný kit pro kvantifikaci knihovny, Illumina™ kompatibilní |
| Agilent ® 2100 Bioanalyzer ® a High Sensitivity DNA Kit (Agilent Technologies Inc.) nebo jiná srovnatelná metoda pro stanovení kvality DNA knihovny | Thermo Scientific MagJET NGS Cleanup a Size Selection Kit (Cat. # K2821) pro čištění nebo výběr velikosti DNA knihovny s požadovanou délkou fragmentu |
Kompletní návod na konstrukci NGS knihovny
A) Úprava konců a připojení adaptérů
V tomto návodu se dozvíte, jak zkonstruovat knihovnu bez amplifikace s použitím 500ng - 1ug vysoce kvalitní fragmentované DNA. Při nižším množství výchozí DNA (5 ng-500 ng) je k dispozici amplifikační protokol (C), který uvidíte níže.
TABULKA 1: Doporučené množství DNA při konstrukci PCR-free knihovny a amplifikované knihovny
| PCR-free knihovna | Amplifikovaná knihovna | |||||
|---|---|---|---|---|---|---|
| Délka čtení NGS knihovny | 50 bp nebo 2 × 25 bp | 300 bp nebo 2 × 150 bp | 500 bp nebo 2× 250 bp | 50 bp nebo 2 x 25 bp | ||
| Střední velikost insertu | ~ 200 bp | ~ 350 bp | ~ 550 bp | ~ 200 bp | ||
| Doporučené množství DNA | 500 ng*-1 μg |
1 μg | 5 ng-1 μg |
|||
Jak upravit konce fragmentované DNA
| Složka | Objem |
| Voda (bez nukleáz) | do 50 μL |
| Fragmentovaná DNA (5ng-1μg) | x μL |
| ClaSeek End Conversion Master Mix, IL | 25 μL |
| Celkem | 50 μL |
- Rozmrazte reakčních složky na ledě, promíchejte a krátce centrifugujte. Roztoky udržujte na ledě.
- Pipetujte všechny složky v daném pořadí do sterilní 0,5ml nebo 0,2ml tenkostěnné zkumavky. Směs udržujte na ledu a následně ji promíchejte vortexováním (3-5 sekund) a krátce centrifugujte.
- Inkubujte reakční směs v termocykleru (teplota víka 100 °C) po dobu 5 minut při teplotě 20°C, 10 minut při 72°C, a nakonec udržujte reakci při teplotě 4°C. Okamžitě pokračujte v dalším kroku (připojení sekvenačních adaptérů).
| Složka | Objem |
| ClaSeek End Conversion reakční směs (z kroku 3) | do 50 μL |
| Adaptéry, Illumina kompatibilní | x μL |
| ClaSeek Ligation Mix, IL |
25 μL |
| Voda (bez nukleáz) | do 70 μL |
| Celkem | 70 μL |
- Do reakční směsi z kroku 3 přidejte Illumina™ kompatibilní adaptéry*, ClaSeek Ligation Mix, IL a vodu. Udržujte směs na ledu. Reakční směs promíchejte vortexováním (3-5 sekund) a krátce centrifugujte.
- Inkubujte reakční směsi při pokojové teplotě (20°C - 25°C) po dobu 5 minut. Pokračujte výběrem velikosti nebo v protokolu pro odstranění adaptérů nebo uskladněte při teplotě -20 °C.
B) Přečištění NGS knihovny a výběr velikosti
DNA knihovna získaná po přidání sekvenačních adaptérů musí být před sekvenováním nebo amplifikací přečištěna pomocí následujícího protokolu pro výběr velikost a odstranění adaptérů.
I. HLAVNÍ PROTOKOL: Výběr velikosti, nebo odstranění adaptérů pomocí magnetických kuliček
Knihovny připravené z 50ng až 1ug výchozí DNA mohou být přečištěny kitem MagJET NGS Cleanup a Size Selection (Cat. #K2821), který umožňuje výběr čisté DNA knihovny přímo připravené pro sekvenování v rámci požadované délky čtení. Tento protokol zajistí odstranění adaptérů. Po výběru velikosti může být proto DNA použita přímo pro sekvenování bez dalšího kroku čištění. Doporučená střední velikost DNA knihovny pro různé délky čtení při sekvenování je uvedena v tabulce 2 níže. U knihoven připravených z menšího množství DNA než 50ng (5ng – 50ng) doporučujeme odstranění adaptérů a přečištění pomocí MagJET NGS Cleanup a Size Selection Kit (Cat. #K2821).
Na co nezapomenout:
- Kity NGS Cleanup a Size Selection (Cat. #K2821) nejsou součástí balení a musí být zakoupeny samostatně.
- Podrobně si pročtěte instrukce pro manipulaci s magnetickými částicemi při použití MagJET NGS Size Selection a Cleanup Kit.
- Zkontrolujte objem ligační reakční směsi obsahující DNA knihovnu (z protokolu Připojení sekvenačních adaptérů) před výběrem velikosti nebo odstranění adaptérů pomocí kitu MagJET a přidejte vodu nebo TE pufru, abyste získali 100ul celkového objemu vzorku DNA.
- Provádějte výběr velikosti DNA knihovny a odstranění adaptérů v 1,5 ml zkumavkách Eppendorf™ LoBind™.
- Vždy aplikujte MagJET kalibrační protokol (MagJET NGS Cleanup a Size Selection Kit, Cat. #K2821) pro stanovení požadovaného objemu vazebného roztoku před výběrem velikosti DNA knihovny.
| Střední velikost insertu | Střední velikost knihovny | Délka čtení |
| ~ 200 bp | 320 bp | 2 × 25 nebo 50 bazí |
| ~ 350 bp | 470 bp | 2 × 150 nebo 300 bazí |
| ~ 550 bp | 670 bp | 2 × 250 nebo 500 bazí |
II. ALTERNATIVNÍ PROTOKOL: Výběr velikosti z agarózového gelu
Při použití tohoto protokolu doporučujeme provést PCR amplifikaci DNA knihovny.
Přečistěte DNA knihovnu s připojenými adaptéry pomocí MagJET NGS Cleanup a Size Selection Kit (Cat. #K2821)(Protokol přečištění) nebo GeneJET NGS Cleanup Kit (Cat. #K0851)(Protokol přečištění). Proveďte eluci vzorku do 25ul elučního pufru.
Připravte 2% agarózový gel (150ml) v 1x TAE, pro barvení použijte SybrGold™ *: přidejte 3g agarózy v prášku do 150ml 1 x TAE pufru, zahřívejte směs v mikrovlnné troubě, dokud se agarózový prášek zcela nerozpustí, nechte chladnout směs po dobu 5-7 minut a přidejte 15ul SybrGold ™ na 150 ml a dobře promíchejte (ředění SybrGold ™ do agarózy / TAE by mělo být 10 000-krát). Nalijte gelovou směs do formy a vložte 12 nebo 16 jamkový hřeben a nechte gel ztuhnout. Doporučené rozměry pro elektroforézní systém: 12 cm × 14 cm (š × v × l), objem pufru 800 ml.
Naneste 15ul žebříčku do první jamky gelu. Nechte jednu jamku prázdnou a naneste vzorek knihovny (2 × 15ul) do dvou sousedních jamek gelu, 15ul do každé jamky. Obdobně, nechte jednu jamku prázdnou před nanesením dalšího vzorku knihovny nebo žebříčku.
| Střední velikost insertu | ~ 200 bp | ~ 350 bp | ~ 550bp |
| Poloha cílového pruhu na gelu | 300-400 bp | 450-550 bp |
650-750 bp |
Izolujte DNA knihovnu o požadované velikosti z gelu pomocí Thermo Scientific GeneJET Gel Extraction a DNA Cleanup Micro Kit (Cat. #K0831/2). Upozorňujeme, že jedna kolonka je určena pro izolaci DNA z ~ 200mg gelu. Pokud je vyříznutý gel větší než 200mg, měl by být rozdělen do dvou kolonek podle instrukcí v manuálu. Proveďte eluci DNA z každé kolonky pomocí 11ul elučního pufru a pak frakce spojte do finálního objemu 20ul. Pokud je vyříznutý gel ≤ 200mg, proveďte přečištění pouze na jedné kolonce a eluci proveďte pomocí 22ul elučního pufru.
- Přečištění knihovny před výběrem velikosti z gelu
- Příprava agarózového gelu
- Naplňte elektroforézní systém pufrem 1x TAE do značky pro maximální objem.
- Přidejte 5ul DNA 6x Loading Dye ke 25ul vzorku DNA knihovny a promíchejte.
- Smíchejte 15ul vody (Nuclease-Free), 5ul DNA 6x Loading Dye a 10ul Thermo Scientific™ O’RangeRuler™ 50 bp DNA ladder (Cat. #SM0613) a promíchejte.
- Nanesení vzorků
- Spusťte gel při 120V konstantním napětím po dobu ~ 120 minut. Zobrazte gel na UV transiluminátoru. Pomocí čistého skalpelu vyřízněte z gelu pruh o šířce dvou jamek, který má velikost v rozmezí 300-400 bp, 450-550 bp a 650-750 bp (v závislosti na požadované délce insertu).
-
Izolujte DNA knihovnu o požadované velikosti z gelu pomocí Thermo Scientific GeneJET Gel Extraction a DNA Cleanup Micro Kit (Cat. #K0831/2). Upozorňujeme, že jedna kolonka je určena pro izolaci DNA z ~ 200mg gelu. Pokud je vyříznutý gel větší než 200mg, měl by být rozdělen do dvou kolonek podle instrukcí v manuálu. Proveďte eluci DNA z každé kolonky pomocí 11ul elučního pufru a pak frakce spojte do finálního objemu 20ul. Pokud je vyříznutý gel ≤ 200mg, proveďte přečištění pouze na jedné kolonce a eluci proveďte pomocí 22ul elučního pufru.
- Izolace DNA z gelu
C) Protokol pro amplifikaci DNA knihovny (dle potřeby)
Tento protokol obsahuje návod pro amplifikaci (zmnožení) DNA knihovny s připojenými adaptéry, která byla připravena z 5 ng až 1 ug výchozího množství DNA pomocí Thermo Scientific ™ Phusion ™ Hot Start II High-Fidelity DNA polymerázy (Cat. #F-549S)*.
| Složka | Objem |
| Voda (bez nukleáz) | do 50 μL |
| 5x Phusion HF Buffer | 10 μL |
| dNTP směs, 2 mM každý | 5 μL (do 0.2 mM) |
| P5 PCR Primer***, 10 μM | 2.5 μL (do 0.5 μM) |
| P7 PCR Primer***, 10 μM | 2.5 μL (do 0.5 μM) |
| Adapter-ligovaná DNA | 10** μL |
| Phusion Hot Start II High-Fidelity DNA Polymerase 2U/μL | 0.5 μL |
| Celkem | 50 μL |
Důležité poznámky: * Phusion Hot Start II High-Fidelity DNA Polymerase, 2U/μL (Cat. #F-549S) není součástí kitu a musí být zakoupena samostatně. ** Objem 20ul se doporučuje při použití adaptér-ligované DNA připravené z méně než 50ng výchozí DNA. *** P5 a P7 PCR primery nejsou součástí kitu a musí být zakoupeny samostatně.
- Přidejte 10 ul ** přečištěné adaptér-ligované DNA knihovny do čisté tenkostěnné 0,2 ml zkumavky. Přidejte následující reagencie v daném pořadí. Směs promíchejte vortexováním (3-5 sekund) a krátce centrifugujte.
- Proveďte PCR podle následujících podmínek (teplota víka 105 °C):
| Teplota | Čas | Cykly / množství DNA |
|---|---|---|
| 98 °C | 30 sec | |
| 98 °C | 10 sec | 6 cyklů / 1μg DNA 8 cyklů / 500ng DNA 10 cyklů / 5-50ng DNA |
| 60 °C | 30 sec | |
| 72 °C | 30 sec | |
| 72 °C | 5 min | |
| 4 °C | hold |
Přečištění amplifikované NGS knihovny
Přečistěte amplifikovanou DNA knihovnu pomocí kitů Thermo Scientific MagJET NGS Size Selection a Cleanup Kit (Protokol pro přečištění). Proveďte eluci DNA knihovny do 22ul elučního pufru. Případně můžete použít Thermo Scientific GeneJET NGS Cleanup Kit (postupujte podle protokolu pro přečištění). Proveďte eluci DNA knihovny do 22ul elučního pufru.
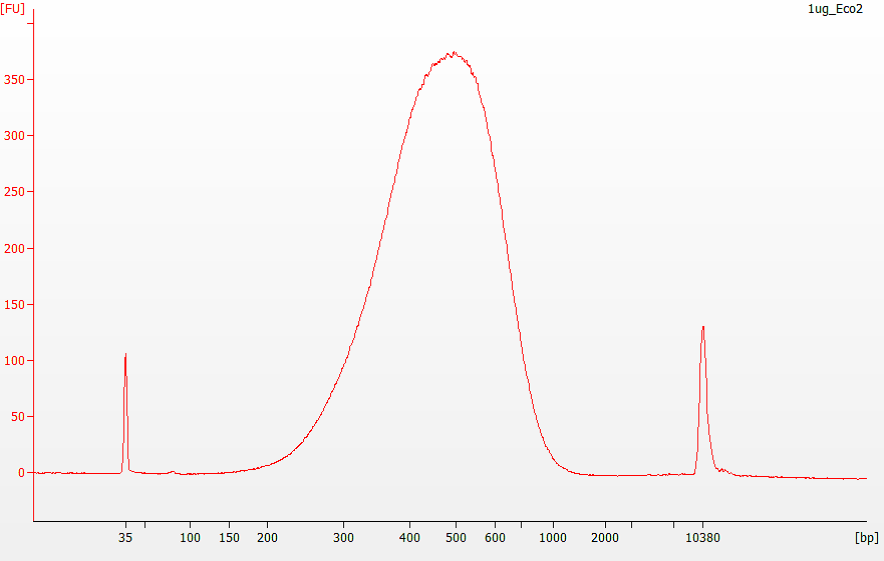
OBRÁZEK 1: Relativní distribuce velikostí DNA fragmentů z E. coli genomové knihovny připravené pomocí kitu ClaSeek Library Preparation (Illumina™ kompatibilní).
500ng a 1ug fragmentované genomové DNA z E. coli bylo použito pro přípravu knihovny bez PCR amplifikace. Výběr velikosti fragmentů z DNA knihovny pro sekvenační délku čtení 300 bazí byl proveden pomocí MagJET NGS Cleanup and Size Selection Kit podle instrukcí v protokolu. Distribuce velikostí fragmentů z obou knihoven (neředěné vzorky) byla analyzována na Agilent 2100 Bioanalyzer pomocí High Sensitivity DNA Kit (Agilent Technologies Inc.)
D) Kvantifikace DNA knihovny
Doporučujeme provádět qPCR kvantifikaci DNA knihoven bez amplifikace a amplifikovaných DNA knihoven před vlastním sekvenováním. Pro kvantifikaci NGS knihoven použijte komerčně dostupné Illumina™ kompatibilní kity. Doporučujeme zředit vzorek DNA knihovny v Tris-HCl 10 mM, pH 8,5 s 0,1% Tween 20. Používejte 10 000-násobné ředění pro kvantifikaci neamplifikované knihovny a 100 000-násobné ředění pro kvantifikaci amplifikované knihovny.
Dále zkontrolujte distribuci velikostí fragmentů připravené DNA knihovny tak, že provedete analýzy na přístroji Agilent 2100 Bioanalyzer pomocí High Sensitivity DNA Kit. Neamplifikované DNA knihovny mohou být analyzovány neředěné. PCR-amplifikované knihovny se ředí 5 - až 10-krát ve vodě bez nukleáz.
Odhadovaná velikost fragmentů u neamplifikované knihovny je podstatně větší (odchylka do ~ 60-100 nt). Atypická migrace fragmentů na čipu je způsobena strukturou Illumina adaptérů ligovaných k oběma koncům DNA fragmentů. Pokud se však provádí PCR amplifikace, migrace fragmentů DNA knihovny je normální a odpovídá očekávané velikosti (střední velikost fragmentů plus 120 bp adaptérů o délce 60 bp ligovaných na obou koncích DNA).